Стекинг и блендинг в ML. Ключевые особенности и реализация с нуля на Python
МЕНЮ
Главная страница
Поиск
Регистрация на сайте
Помощь проекту
Архив новостей
ТЕМЫ
Новости ИИ
Городские сумасшедшие
ИИ в медицине
ИИ проекты
Искусственные нейросети
Искусственный интеллект
Слежка за людьми
Угроза ИИ
ИИ теория
Компьютерные науки
Машинное обуч. (Ошибки)
Машинное обучение
Машинный перевод
Нейронные сети начинающим
Психология ИИ
Реализация ИИ
Реализация нейросетей
Создание беспилотных авто
Трезво про ИИ
Философия ИИ
Генетические алгоритмы
Капсульные нейросети
Основы нейронных сетей
Промпты. Генеративные запросы
Распознавание лиц
Распознавание образов
Распознавание речи
Творчество ИИ
Техническое зрение
Чат-боты
Авторизация
2024-03-11 21:44

Среди всех методов ансамблирования особое внимание заслуживают две очень мощные техники, известные как стекинг (stacked generalization) и блендинг, особенность которых заключается в возможности использования прогнозов не только однородных, но и сразу нескольких разных по природе алгоритмов в качестве обучающих данных для другой модели, на которой будет сделан итоговый прогноз. Например, прогнозы логистической регрессии и градиентного бустинга могут быть использованы для обучения случайного леса, на котором уже будет выполнен итоговый прогноз.
Стекинг и блендинг очень схожи между собой, однако между ними есть существенные различия, заключающиеся в разделении и использовании тренировочных данных. Рассмотрим более подробно как это происходит.
Ноутбук с данными алгоритмами можно загрузить на Kaggle (eng) и GitHub (rus).
Stacking
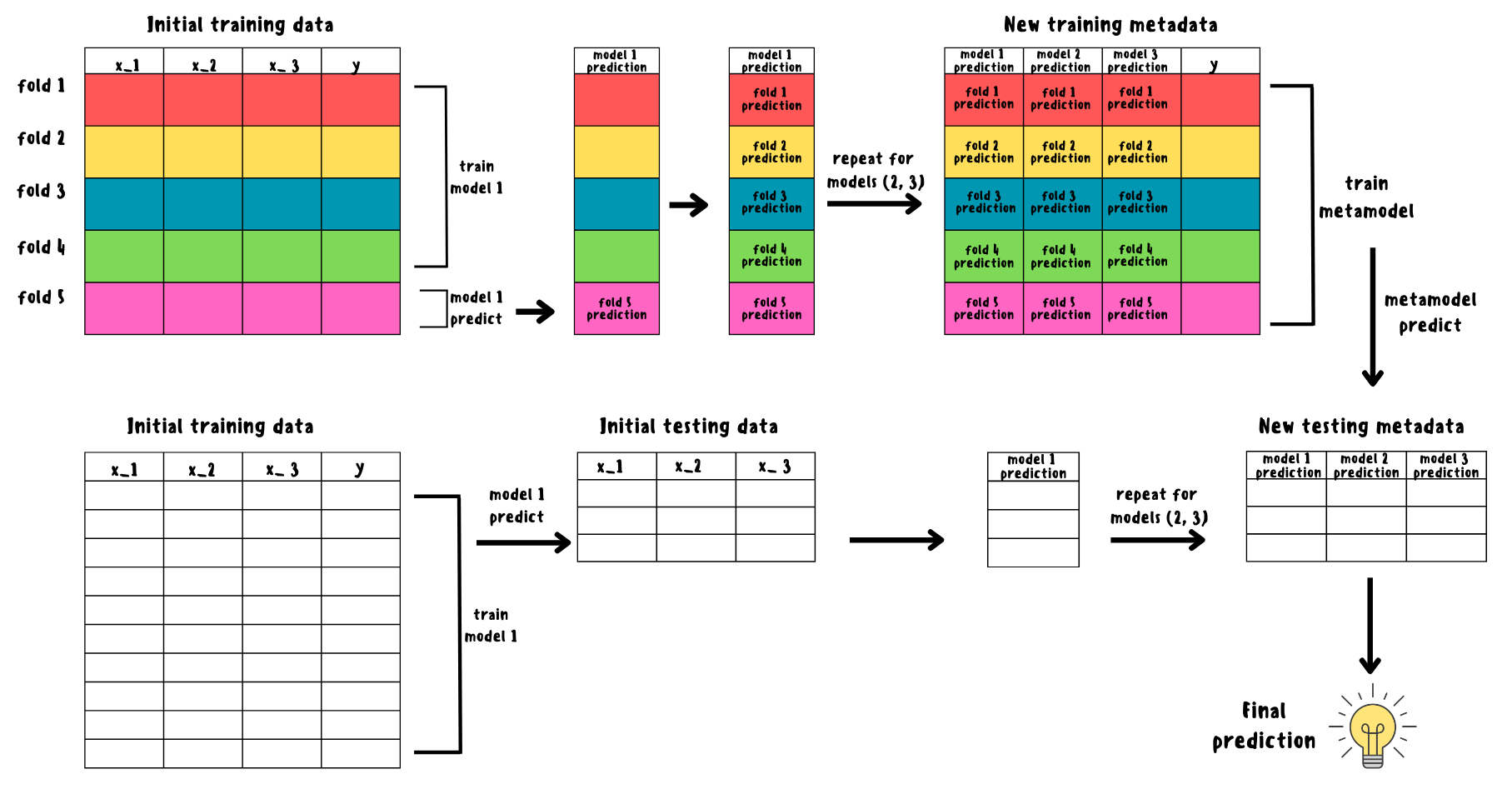
Изначально датасет разбивается на тренировочный и тестовый. Далее с помощью k-fold кросс-валидации тренировочный датасет разбивается на k фолдов. Базовая модель обучается на k-1 фолдах и делает прогноз на оставшемся. Данная процедура повторяется для каждого фолда и в итоге получится вектор, состоящий из k-fold прогнозов и используемый как новый признак. Предыдущие шаги повторяются для каждой базовой модели и в итоге получится набор признаков, состоящий из прогнозов базовых моделей, к которым добавляется таргет y_train из исходного тренировочного датасета и полученный датасет будет новым тренировочным. Помимо этого, базовые модели также обучаются на всём исходном тренировочном множестве, после чего делается прогноз на тестовом датасете и в итоге получится новый тестовый набор.
На полученных датасетах (метаданных) обучается метамодель и производится итоговый прогноз.
Blending
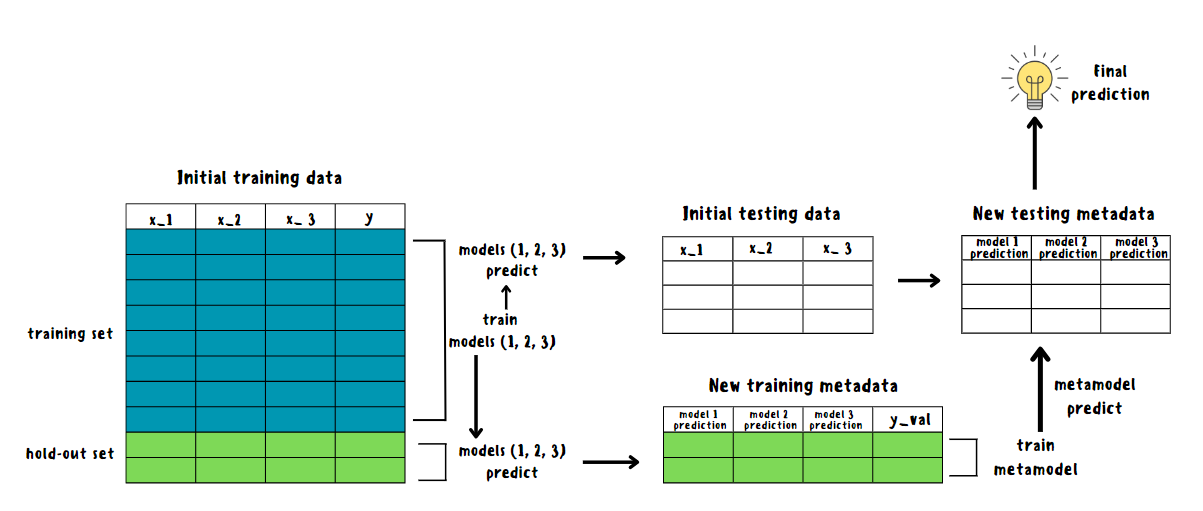
Блендинг является более простой версией стекинга. Тренировочные данные разделяются на 2 части: также на тренировочную и валидационную с помощью hold-out кросс-валидации. Базовая модель обучается на тренировочных данных и делает прогноз как на валидационном, так и на тестовом наборе. Далее предыдущий шаг повторяется для каждой базовой модели: к прогнозам на валидационном наборе добавляется таргет y_val и полученный датасет используется в качестве тренировочного, а прогнозы на тестовом наборе используются в качестве нового тестового.
На полученных датасетах (метаданных) обучается метамодель и производится итоговый прогноз.
Более продвинутые техники
Для ускорения работы стекинга и блендинга на практике используется параллелизация во время обучения, то есть каждая базовая модель может обучаться на разных ядрах параллельно. Нетрудно догадаться, что такой подход является особенно полезным при работе с большими наборами данных или сложными моделями. В реализации scikit-learn параллелизация реализована с помощью библиотеки joblib, а количество используемых ядер устанавливается с помощью параметра n_jobs (при значении -1 используются все доступные ядра). В ручной реализации ниже также применяется параллельное обучение.
Ещё стоит добавить, что существуют и другие версии стекинга и блендинга, например, когда новые метаданные добавляются к исходным. Помимо этого, стекинг и блендинг могут быть многослойными, когда на каждом уровне объединяются прогнозы моделей, полученные на предыдущем, а затем эти объединённые прогнозы используются для обучения новых моделей на следующем уровне. Иногда такой подход может дать неплохой прирост в плане точности, но стоит иметь в виду, что в таком случае время обучения также заметно увеличится.
На данный момент в scikit-learn реализована поддержка напрямую лишь для стекинга, однако, если выбрать 1 фолд для кросс-валидации и обучить базовые модели отдельно, то можно отдалённо получить что-то похожее на блендинг.
Импорт необходимых библиотек
import numpy as np import pandas as pd import matplotlib.pyplot as plt from sklearn.datasets import load_diabetes from sklearn.preprocessing import LabelEncoder from sklearn.metrics import accuracy_score, mean_absolute_percentage_error from sklearn.model_selection import train_test_split, cross_val_predict from sklearn.svm import SVC from sklearn.linear_model import RidgeCV, LogisticRegression from sklearn.ensemble import StackingClassifier, StackingRegressor from sklearn.ensemble import RandomForestClassifier, RandomForestRegressor from sklearn.ensemble import GradientBoostingClassifier, GradientBoostingRegressor from joblib import Parallel, delayed from mlxtend.plotting import plot_decision_regionsРеализация на Python с нуля
class Stacking: def __init__(self, estimators, final_estimator, blending=False, cv=5, n_jobs=-1): self.estimators = estimators self.final_estimator = final_estimator self.blending = blending self.cv = cv self.n_jobs = n_jobs def _X_pred(self, estimator, data): if self.blending: X_train_v, y_train_v, X_val = data return estimator.fit(X_train_v, y_train_v).predict(X_val) else: X_train, y_train = data return cross_val_predict(estimator, X_train, y_train, cv=self.cv) def _X_test_pred(self, estimator, data): X_train, y_train, X_test = data return estimator.fit(X_train, y_train).predict(X_test) def _meta_data(self, X_train, y_train, X_test): if self.blending: #used hold-out cross-validation X_train_v, X_val, y_train_v, y_val = train_test_split(X_train, y_train, random_state=0) train_data = [X_train_v, y_train_v, X_val] test_data = [X_train_v, y_train_v, X_test] meta_y_train = y_val else: train_data = [X_train, y_train] test_data = [X_train, y_train, X_test] meta_y_train = y_train cv_X_train_preds = (delayed(self._X_pred)(est, train_data) for est in self.estimators) X_test_preds = (delayed(self._X_test_pred)(est, test_data) for est in self.estimators) meta_X_train = pd.DataFrame(Parallel(n_jobs=self.n_jobs)(cv_X_train_preds)) meta_X_test = pd.DataFrame(Parallel(n_jobs=self.n_jobs)(X_test_preds)) return meta_X_train.T, meta_y_train, meta_X_test.T def fit_predict(self, X_train, y_train, X_test): # meta learner or blender meta_X_train, meta_y_train, meta_X_test = self._meta_data(X_train, y_train, X_test) return self.final_estimator.fit(meta_X_train, meta_y_train).predict(meta_X_test)Код для отрисовки графика
def decision_boundary_plot(X, y, X_train, y_train, clf, feature_indexes, title=None): feature1_name, feature2_name = X.columns[feature_indexes] X_feature_columns = X.values[:, feature_indexes] X_train_feature_columns = X_train.values[:, feature_indexes] clf.fit(X_train_feature_columns, y_train.values) plot_decision_regions(X=X_feature_columns, y=y.values, clf=clf) plt.xlabel(feature1_name) plt.ylabel(feature2_name) plt.title(title)Загрузка датасетов
Для обучения моделей будет использован Glass Classification датасет, где необходимо верно определить тип стекла по его признакам. В случае регрессии используется Diabetes датасет из scikit-learn.
df_path = "/content/drive/MyDrive/glass.csv" glass_df = pd.read_csv(df_path) X1, y1 = glass_df.iloc[:, :-1], glass_df.iloc[:, -1] y1 = pd.Series(LabelEncoder().fit_transform(y1)) X1_train, X1_test, y1_train, y1_test = train_test_split(X1, y1, random_state=0) print(glass_df) RI Na Mg Al Si K Ca Ba Fe Type 0 1.52101 13.64 4.49 1.10 71.78 0.06 8.75 0.00 0.0 1 1 1.51761 13.89 3.60 1.36 72.73 0.48 7.83 0.00 0.0 1 2 1.51618 13.53 3.55 1.54 72.99 0.39 7.78 0.00 0.0 1 3 1.51766 13.21 3.69 1.29 72.61 0.57 8.22 0.00 0.0 1 4 1.51742 13.27 3.62 1.24 73.08 0.55 8.07 0.00 0.0 1 .. ... ... ... ... ... ... ... ... ... ... 209 1.51623 14.14 0.00 2.88 72.61 0.08 9.18 1.06 0.0 7 210 1.51685 14.92 0.00 1.99 73.06 0.00 8.40 1.59 0.0 7 211 1.52065 14.36 0.00 2.02 73.42 0.00 8.44 1.64 0.0 7 212 1.51651 14.38 0.00 1.94 73.61 0.00 8.48 1.57 0.0 7 213 1.51711 14.23 0.00 2.08 73.36 0.00 8.62 1.67 0.0 7 [214 rows x 10 columns]X2, y2 = load_diabetes(return_X_y=True, as_frame=True) X2_train, X2_test, y2_train, y2_test = train_test_split(X2, y2, random_state=0) print(X2, y2, sep=' ') age sex bmi bp s1 s2 s3 0 0.038076 0.050680 0.061696 0.021872 -0.044223 -0.034821 -0.043401 1 -0.001882 -0.044642 -0.051474 -0.026328 -0.008449 -0.019163 0.074412 2 0.085299 0.050680 0.044451 -0.005670 -0.045599 -0.034194 -0.032356 3 -0.089063 -0.044642 -0.011595 -0.036656 0.012191 0.024991 -0.036038 4 0.005383 -0.044642 -0.036385 0.021872 0.003935 0.015596 0.008142 .. ... ... ... ... ... ... ... 437 0.041708 0.050680 0.019662 0.059744 -0.005697 -0.002566 -0.028674 438 -0.005515 0.050680 -0.015906 -0.067642 0.049341 0.079165 -0.028674 439 0.041708 0.050680 -0.015906 0.017293 -0.037344 -0.013840 -0.024993 440 -0.045472 -0.044642 0.039062 0.001215 0.016318 0.015283 -0.028674 441 -0.045472 -0.044642 -0.073030 -0.081413 0.083740 0.027809 0.173816 s4 s5 s6 0 -0.002592 0.019907 -0.017646 1 -0.039493 -0.068332 -0.092204 2 -0.002592 0.002861 -0.025930 3 0.034309 0.022688 -0.009362 4 -0.002592 -0.031988 -0.046641 .. ... ... ... 437 -0.002592 0.031193 0.007207 438 0.034309 -0.018114 0.044485 439 -0.011080 -0.046883 0.015491 440 0.026560 0.044529 -0.025930 441 -0.039493 -0.004222 0.003064 [442 rows x 10 columns] 0 151.0 1 75.0 2 141.0 3 206.0 4 135.0 ... 437 178.0 438 104.0 439 132.0 440 220.0 441 57.0 Name: target, Length: 442, dtype: float64Обучение моделей и оценка полученных результатов
Как в случае классификации, так и регрессии, стекинг и блендинг показали одинаковые и не самые лучшие результаты. Как правило, такая ситуация происходит по двум причинам: учитывая, что метаданные строятся на прогнозах базовых моделей, то наличие слабых базовых моделей может снизить точность более сильных, что снизит итоговый прогноз в целом; также небольшое количество тренировочных данных часто приводит к переобучению, что в свою очередь снижает точность прогнозов.
В данном случае проблему можно частично решить, установив stack_method='predict_proba', когда каждый базовый классификатор выдаёт вероятности принадлежности к классам вместо самих классов, что может помочь увеличить точность в случае с не взаимоисключающими классами; также такой метод лучше работает с шумом в данных. Как можно заметить, данный способ позволил существенно увеличить точность модели. При правильном подборе моделей и гиперпараметров точность будет ещё выше.
Чаще всего стекинг показывает немного лучшие результаты чем блендинг из-за применения k-fold кросс-валидации, но обычно разница заметна лишь на большом количестве данных.
StackingClassifier & BlendingClassifier
estimators = [LogisticRegression(random_state=0, max_iter=10000), GradientBoostingClassifier(random_state=0), SVC(probability=True, random_state=0)] estimator = RandomForestClassifier(random_state=0) stacking_clf = Stacking(estimators=estimators, final_estimator=estimator) stacking_pred_res = stacking_clf.fit_predict(X1_train, y1_train, X1_test) stacking_accuracy = accuracy_score(stacking_pred_res, y1_test) print(f'stacking_accuracy: {stacking_accuracy}') print(stacking_pred_res, '', sep=' ') blending_clf = Stacking(estimators=estimators, final_estimator=estimator, blending=True) blending_pred_res = blending_clf.fit_predict(X1_train, y1_train, X1_test) blending_accuracy = accuracy_score(blending_pred_res, y1_test) print(f'blending_accuracy: {blending_accuracy}') print(blending_pred_res) stacking_accuracy: 0.6481481481481481 [5 0 1 4 1 1 0 1 1 1 1 0 1 1 1 5 0 1 0 0 3 0 5 5 0 0 5 0 0 1 0 0 1 0 1 0 0 0 0 5 3 4 1 0 1 1 0 1 0 1 0 4 5 0] blending_accuracy: 0.6481481481481481 [5 0 1 4 1 1 0 1 1 1 1 0 1 1 1 5 0 1 0 1 5 1 5 5 1 0 5 0 1 1 0 0 1 0 0 0 0 0 0 5 3 5 1 0 1 1 0 1 0 1 0 4 5 0]StackingClassifier (scikit-learn) с визуализацией решающих границ
sk_estimators = [('lr', LogisticRegression(random_state=0, max_iter=10000)), ('gbc', GradientBoostingClassifier(random_state=0)), ('svc', SVC(probability=True, random_state=0))] stack_methods = ('predict', 'predict_proba') estimator = RandomForestClassifier(random_state=0) sk_stacking_clf = StackingClassifier(estimators=sk_estimators, final_estimator=estimator) feature_indexes = [1, 3] plt.figure(figsize=(12, 5)) for i, method in enumerate(stack_methods): sk_stacking_clf.stack_method = method sk_stacking_clf.fit(X1_train, y1_train) sk_stacking_pred_res = sk_stacking_clf.predict(X1_test) sk_stacking_accuracy = accuracy_score(sk_stacking_pred_res, y1_test) print(f'sk_stacking_accuracy with a {method} method: {sk_stacking_accuracy}') print(sk_stacking_pred_res) plt.subplot(1, 2, i + 1) plt.subplots_adjust(hspace=1.5) title = f'StackingClassifier surface with a {method} method' decision_boundary_plot(X1, y1, X1_train, y1_train, sk_stacking_clf, feature_indexes, title) sk_stacking_accuracy with a predict method: 0.6481481481481481 [5 0 1 4 1 1 0 1 1 1 1 0 1 1 1 5 0 1 0 0 3 0 5 5 0 0 5 0 0 1 0 0 1 0 1 0 0 0 0 5 3 4 1 0 1 1 0 1 0 1 0 4 5 0] sk_stacking_accuracy with a predict_proba method: 0.7592592592592593 [5 0 1 4 3 1 0 1 1 1 1 0 1 1 1 5 0 1 2 2 3 0 5 5 1 0 5 0 1 1 0 0 1 0 1 0 0 2 0 5 5 4 1 0 1 1 0 1 0 1 0 4 5 0]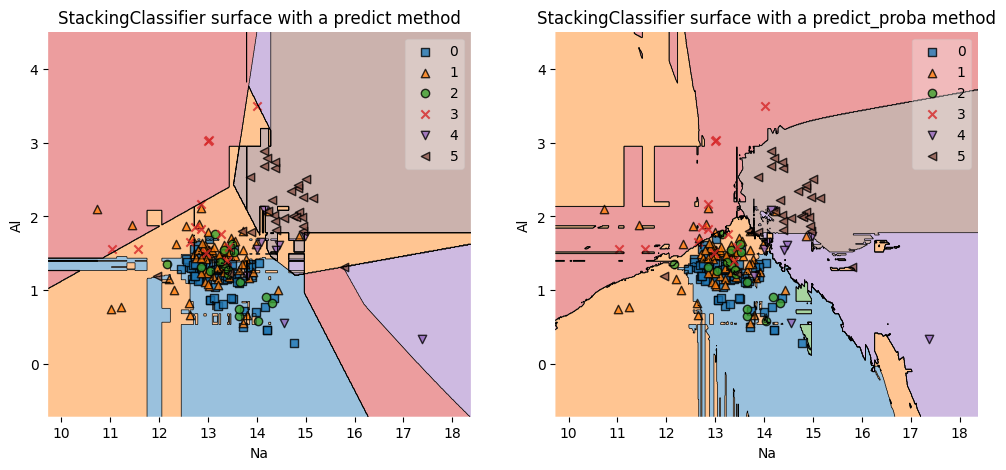
StackingRegressor & StackingRegressor (scikit-learn)
reg_estimators = [RandomForestRegressor(random_state=0), GradientBoostingRegressor(random_state=0)] stacking_reg = Stacking(estimators=reg_estimators, final_estimator=RidgeCV()) stacking_reg_pred_res = stacking_reg.fit_predict(X2_train, y2_train, X2_test) stacking_mape = mean_absolute_percentage_error(stacking_reg_pred_res, y2_test) print(f'stacking_regressor_mape {stacking_mape}') print(stacking_reg_pred_res, '', sep=' ') sk_reg_estimators = [('rfr', RandomForestRegressor(random_state=0)), ('gbr', GradientBoostingRegressor(random_state=0))] sk_stacking_reg = StackingRegressor(estimators=sk_reg_estimators) sk_stacking_reg.fit(X2_train, y2_train) sk_stacking_reg_pred_res = sk_stacking_reg.predict(X2_test) sk_stacking_mape = mean_absolute_percentage_error(sk_stacking_reg_pred_res, y2_test) print(f'sk_stacking_regressor_mape {sk_stacking_mape}') print(sk_stacking_reg_pred_res) stacking_regressor_mape 0.3294355656302654 [248.19759057 240.42764024 177.37191492 103.86233455 200.13250024 250.97352765 96.82048975 220.71264013 131.5200259 236.41159677 175.71519802 160.35569454 130.9100711 93.65232358 282.06237765 99.93621948 161.47206754 78.65895059 108.86806694 224.46260151 182.68564834 127.54111953 163.28785267 138.89063619 220.53939703 189.84079506 136.98136758 78.91556812 219.66245835 159.14526636 198.39205847 82.77579781 117.59833274 157.49622357 139.53979064 171.05953707 152.42297469 135.62774138 94.81503188 213.49660018 110.36059875 162.00479518 132.07261264 178.57636808 179.29614901 73.3945309 114.601665 131.93470279 100.32309962 252.57462411 146.00870076 61.92053404 170.56742259 157.92964414 243.28628037 205.27588938 180.79716523 114.89480581 120.80464762 172.87785542 243.4033502 151.64437003 130.09006375 100.99049563 249.91693845 153.00241663 87.45729779 230.20145421 215.78130712 90.82440238 88.24276622 143.91478174 110.89538069 134.84971688 130.50875598 177.97770535 121.87554552 221.70653117 261.76922106 197.7323525 125.88596841 191.96118205 71.8331337 240.12385544 129.00872186 89.92647528 151.49862554 202.71572059 105.9398957 150.37365076 103.92670222 108.23845662 87.0924303 168.01234827 106.55530568 93.81879887 232.8935379 238.29278058 136.22349466 154.71341867 157.80577109 114.83038143 159.25202218 100.13701043 236.14776543 143.92620712 235.19141566 269.14119287 113.39076553 86.51606237 251.53999411] sk_stacking_regressor_mape 0.3294355656302654 [248.19759057 240.42764024 177.37191492 103.86233455 200.13250024 250.97352765 96.82048975 220.71264013 131.5200259 236.41159677 175.71519802 160.35569454 130.9100711 93.65232358 282.06237765 99.93621948 161.47206754 78.65895059 108.86806694 224.46260151 182.68564834 127.54111953 163.28785267 138.89063619 220.53939703 189.84079506 136.98136758 78.91556812 219.66245835 159.14526636 198.39205847 82.77579781 117.59833274 157.49622357 139.53979064 171.05953707 152.42297469 135.62774138 94.81503188 213.49660018 110.36059875 162.00479518 132.07261264 178.57636808 179.29614901 73.3945309 114.601665 131.93470279 100.32309962 252.57462411 146.00870076 61.92053404 170.56742259 157.92964414 243.28628037 205.27588938 180.79716523 114.89480581 120.80464762 172.87785542 243.4033502 151.64437003 130.09006375 100.99049563 249.91693845 153.00241663 87.45729779 230.20145421 215.78130712 90.82440238 88.24276622 143.91478174 110.89538069 134.84971688 130.50875598 177.97770535 121.87554552 221.70653117 261.76922106 197.7323525 125.88596841 191.96118205 71.8331337 240.12385544 129.00872186 89.92647528 151.49862554 202.71572059 105.9398957 150.37365076 103.92670222 108.23845662 87.0924303 168.01234827 106.55530568 93.81879887 232.8935379 238.29278058 136.22349466 154.71341867 157.80577109 114.83038143 159.25202218 100.13701043 236.14776543 143.92620712 235.19141566 269.14119287 113.39076553 86.51606237 251.53999411]Преимущества и недостатки стекинга и блендинга
Преимущества:
-
значительное улучшение точности прогнозов при правильном использовании.
Недостатки:
-
высокие вычислительные затраты;
-
возможность переобучения из-за трудностей в правильном подборе и настройке базовых моделей, а также сложность в интерпретации.
Дополнительные источники
Статья «An Interpretation of Stacking and Blending Approach in Machine Learning», Divya Khyani, Soumya Jakkula, Sanjana Gowda N C, Anusha K J, Swetha K R.
Документация:
Метод главных компонент ?
Телеграм: t.me/ainewsline
Источник: habr.com