Кластеризация с пакетом ClusterR, часть 1
МЕНЮ
Главная страница
Поиск
Регистрация на сайте
Помощь проекту
Архив новостей
ТЕМЫ
Новости ИИ
Голосовой помощник
Городские сумасшедшие
ИИ в медицине
ИИ проекты
Искусственные нейросети
Искусственный интеллект
Слежка за людьми
Угроза ИИ
Разработка ИИГородские сумасшедшие
ИИ в медицине
ИИ проекты
Искусственные нейросети
Искусственный интеллект
Слежка за людьми
Угроза ИИ
Атаки на ИИ
ИИ теория
Компьютерные науки
Машинное обуч. (Ошибки)
Машинное обучение
Машинный перевод
Нейронные сети начинающим
Психология ИИ
Реализация ИИ
Реализация нейросетей
Создание беспилотных авто
Трезво про ИИ
Философия ИИ
Внедрение ИИИИ теория
Компьютерные науки
Машинное обуч. (Ошибки)
Машинное обучение
Машинный перевод
Нейронные сети начинающим
Психология ИИ
Реализация ИИ
Реализация нейросетей
Создание беспилотных авто
Трезво про ИИ
Философия ИИ
Big data
Генетические алгоритмы
Капсульные нейросети
Основы нейронных сетей
Промпты. Генеративные запросы
Распознавание лиц
Распознавание образов
Распознавание речи
Творчество ИИ
Техническое зрение
Чат-боты
Работа разума и сознаниеМодель мозгаРобототехника, БПЛАТрансгуманизмОбработка текстаТеория эволюцииДополненная реальностьЖелезоКиберугрозыНаучный мирИТ индустрияРазработка ПОТеория информацииМатематикаЦифровая экономика
Генетические алгоритмы
Капсульные нейросети
Основы нейронных сетей
Промпты. Генеративные запросы
Распознавание лиц
Распознавание образов
Распознавание речи
Творчество ИИ
Техническое зрение
Чат-боты
Авторизация
2016-09-26 21:30

Эта статья посвящена кластеризации, а точнее, моему недавно добавленному в CRAN пакету ClusterR. Детали и примеры ниже в большинстве своем основаны на пакете Vignette.
Кластерный анализ или кластеризация - задача группирования набора объектов таким образом, чтобы объекты внутри одной группы (называемой кластером) были более похожи (в том или ином смысле) друг на друга, чем на объекты в других группах (кластерах). Это одна из главных задач исследовательского анализа данных и стандартная техника статистического анализа, применяемая в разных сферах, в т.ч. машинном обучении, распознавании образов, анализе изображений, поиске информации, биоинформатике, сжатии данных, компьютерной графике.
Наиболее известные примеры алгоритмов кластеризации - кластеризация на основе связности (иерархическая кластеризация), кластеризация на основе центров (метод k-средних, метод k-медоидов), кластеризация на основе распределений (GMM - Gaussian mixture models - Гауссова смесь распределений) и кластеризация на основе плотности (DBSCAN - Density-based spatial clustering of applications with noise - пространственная кластеризация приложений с шумом на основе плотности, OPTICS - Ordering points to identify the clustering structure - упорядочивание точек для определения структуры кластеризации, и др.).
Пакет ClusterR состоит из алгоритмов кластеризации на основе центров (метод k-средних, k-средних в мини-группах, k-медоидов) и распределений (GMM). Также пакет предлагает функции для:
Гауссова смесь распределений - статистическая модель для представления нормально распределенных субпопуляций внутри общей популяции. Гауссова смесь распределений параметризируется двумя типами значений - смесь весов компонентов и средних компонентов или ковариаций (для многомерного случая). Если количество компонентов известно, техника, чаще всего используемая для оценки параметров смеси распределений - ЕМ-алгоритм.
Функция GMM в пакете ClusterR - реализация на R класса для моделирования данных как гауссовой смеси распределений (GMM) из библиотеки Armadillo с предположением о диагональных ковариационных матрицах. Можно настраивать параметры функции, в том числе gaussian_comps, dist_mode (eucl_dist, maha_dist), seed_mode (static_subset, random_subset, static_spread, random_spread), km_iter и em_iter (больше информации о параметрах в документации к пакету). Проиллюстрирую функцию GMM на синтетических данных dietary_survey_IBS.
Исходно функция GMM возвращает центроиды, матрицу ковариации (где каждая строка представляет диагональную ковариационную матрицу), веса и логарифмические функции правдоподобия для каждой гауссовой компоненты. Затем функция predict_GMM берет выходные данные модели GMM и возвращает вероятные кластеры.
В дополнение к уже упомянутым функциям можно использовать Optimal_Clusters_GMM для оценки количества кластеров данных с помощью или информационного критерия Акаике (AIC, Akaike information), или байесовского информационного критерия (BIC, Bayesian information).
При выборе модели из предопределенного множества предпочтительнее выбирать ту, у которой самый низкий BIC, здесь это справедливо для количества кластеров, равного 2.
Предполагая, что доступны метки истинности, для валидации выходных кластеров можно использовать методы external_validation (rand_index, adjusted_rand_index, jaccard_index, fowlkes_Mallows_index, mirkin_metric, purity, entropy, nmi (нормализованная взаимная информация) и var_info (вариация информации).
И если параметр summary_stats установлен в TRUE, то возвращаются также метрики специфичности, чувствительности, точности, полноты, F-меры (specificity, sensitivity, precision, recall, F-measure соответственно).
Кластеризация методом k-средних - метод векторного квантования, исходно применяемый в обработке сигналов, часто используется для кластерного анализа данных. Цель кластеризации методом k-средних - разделить n значений на k кластеров, в которых каждое значение принадлежит кластеру с ближайшим средним, выступающим прототипом кластера. Это приводит к разделению области данных на ячейки Вороного. Наиболее часто применяемый алгоритм использует итеративную уточняющую технику. Из-за повсеместного употребления, его называют алгоритмом k-средних; в частности, среди специалистов в сфере компьютерных наук он также известен как алгоритм Ллойда.
Пакет ClusterR предоставляет две разных функции k-средних, KMeans_arma, реализацию на R метода k-средних из библиотеки armadillo, и KMeans_rcpp, которая использует пакет RcppArmadillo. Обе функции приводят к одним и тем же результатам, однако, возвращают разные признаки (код ниже иллюстрирует это).
KMeans_arma быстрее, чем функция KMeans_rcpp, однако, исходно она выводит центроиды только некоторых кластеров. Более того, количество колонок в данных должно превышать количество кластеров, иначе функция вернет ошибку. Кластеризация будет работать быстрее на многоядерных машинах с включенным OpenMP (например, -fopenmp в GCC). Алгоритм инициализируется один раз, и обычно 10 итераций достаточно для сходимости. Исходные центроиды распределяются с помощью одного из алгоритмов - keep_existing, static_subset, random_subset, static_spread или random_spread. Если seed_mode равно keep_existing, пользователь должен передать на вход матрицу центроидов.
Я уменьшу количество измерений в данных dietary_survey_IBS с помощью анализа главных компонент (PCA - principal component analysis), а именно - функции princomp из пакета stats, чтобы можно было вывести двумерный график кластеров, построенных в результате.
Как утверждалось выше, функция KMeans_rcpp предлагает некоторые дополнительные возможности по сравнению с функцией KMeans_arma:
Больше подробностей о KMeans_rcpp есть в документации пакета. Проиллюстрирую разные параметры KMeans_rcpp на примере векторного квантования и пакета OpenImageR.

Атрибут between.SS_DIV_total.SS равен (total_SSE - sum(WCSS_per_cluster)) / total_SSE. Если в кластеризации нет закономерности, промежуточная сумма квадратов будет очень небольшой частью общей суммы квадратов, а если атрибут between.SS_DIV_total.SS близок к 1.0, значения кластеризуются достаточно хорошо.

Кроме того, можно воспользоваться функцией Optimal_Clusters_KMeans (которая неявно использует KMeans_rcpp), чтобы определить оптимальное количество кластеров. Доступны такие критерии: variance_explained, WCSSE (within-cluster-sum-of-squared-error - сумма-квадратов-ошибок-внутри-кластера), dissimilarity, silhouette, distortion_fK, AIC, BIC и Adjusted_Rsquared. В документации по пакету есть больше информации по каждому критерию.
В следующем примере кода используется критерий distortion_fK, который полностью описан в статье -Selection of K in K-means clustering, Pham., Dimov., Nguyen., (2004)- («Выбор К в кластеризации методом К-средних»).
Значения меньше фиксированной границы (здесь fK_threshold = 0.85) можно рекомендовать для кластеризации. Однако, существует более одного оптимального разбиения на кластеры, поэтому f(K) следует использовать только для предположения об их количестве, но окончательное решение, принимать это значение или нет - за пользователем.
Метод k-средних в мини-группах - вариация классического алгоритма k-средних. Он особенно полезен для больших наборов данных, поскольку вместо использования всего набора (как в k-средних) берутся мини-группы из случайных значений данных, чтобы оптимизировать целевую функцию.
Параметры алгоритма MiniBatchKmeans почти такие же, как и функции KMeans_rcpp из пакета ClusterR. Наиболее важная разница - параметр batch_size (размер мини-групп) и init_fraction (процент данных для определения исходных центроидов, который применяется, если initializer равен -kmeans++- или -quantile_init-).
Воспользуюсь примером векторного квантования, чтобы показать разницу во времени вычисления и качестве вывода функций KMeans_rcpp и MiniBatchKmeans.

Сначала выполним кластеризацию k-средних.

Теперь кластеризацию k-средних в мини-группах.

Несмотря на небольшую разницу в качестве вывода, k-средних в мини-группах возвращает результат в среднем в два раза быстрее, чем классический метод k-средних для этого набора данных.
Чтобы реализовать метод k-средних в мини-группах, я использовал следующие ресурсы:
Кластерный анализ или кластеризация - задача группирования набора объектов таким образом, чтобы объекты внутри одной группы (называемой кластером) были более похожи (в том или ином смысле) друг на друга, чем на объекты в других группах (кластерах). Это одна из главных задач исследовательского анализа данных и стандартная техника статистического анализа, применяемая в разных сферах, в т.ч. машинном обучении, распознавании образов, анализе изображений, поиске информации, биоинформатике, сжатии данных, компьютерной графике.
Наиболее известные примеры алгоритмов кластеризации - кластеризация на основе связности (иерархическая кластеризация), кластеризация на основе центров (метод k-средних, метод k-медоидов), кластеризация на основе распределений (GMM - Gaussian mixture models - Гауссова смесь распределений) и кластеризация на основе плотности (DBSCAN - Density-based spatial clustering of applications with noise - пространственная кластеризация приложений с шумом на основе плотности, OPTICS - Ordering points to identify the clustering structure - упорядочивание точек для определения структуры кластеризации, и др.).
Пакет ClusterR состоит из алгоритмов кластеризации на основе центров (метод k-средних, k-средних в мини-группах, k-медоидов) и распределений (GMM). Также пакет предлагает функции для:
- валидации выходных данных с помощью меток истинности;
- вывода результатов на контурном или двумерном графике;
- предсказания новых результатов наблюдений;
- оценки оптимального числа кластеров для каждого отдельного алгоритма.
Гауссова смесь распределений (GMM - Gaussian mixture models)
Гауссова смесь распределений - статистическая модель для представления нормально распределенных субпопуляций внутри общей популяции. Гауссова смесь распределений параметризируется двумя типами значений - смесь весов компонентов и средних компонентов или ковариаций (для многомерного случая). Если количество компонентов известно, техника, чаще всего используемая для оценки параметров смеси распределений - ЕМ-алгоритм.
Функция GMM в пакете ClusterR - реализация на R класса для моделирования данных как гауссовой смеси распределений (GMM) из библиотеки Armadillo с предположением о диагональных ковариационных матрицах. Можно настраивать параметры функции, в том числе gaussian_comps, dist_mode (eucl_dist, maha_dist), seed_mode (static_subset, random_subset, static_spread, random_spread), km_iter и em_iter (больше информации о параметрах в документации к пакету). Проиллюстрирую функцию GMM на синтетических данных dietary_survey_IBS.
library(ClusterR) data(dietary_survey_IBS) dim(dietary_survey_IBS) ## [1] 400 43 X = dietary_survey_IBS[, -ncol(dietary_survey_IBS)] # данные (без зависимой переменной) y = dietary_survey_IBS[, ncol(dietary_survey_IBS)] # зависимая переменная dat = center_scale(X, mean_center = T, sd_scale = T) # центрирование и масштабирование данных gmm = GMM(dat, 2, dist_mode = "maha_dist", seed_mode = "random_subset", km_iter = 10, em_iter = 10, verbose = F) # предсказание центроидов, ковариационной матрицы и весов pr = predict_GMM(dat, gmm$centroids, gmm$covariance_matrices, gmm$weights) Исходно функция GMM возвращает центроиды, матрицу ковариации (где каждая строка представляет диагональную ковариационную матрицу), веса и логарифмические функции правдоподобия для каждой гауссовой компоненты. Затем функция predict_GMM берет выходные данные модели GMM и возвращает вероятные кластеры.
В дополнение к уже упомянутым функциям можно использовать Optimal_Clusters_GMM для оценки количества кластеров данных с помощью или информационного критерия Акаике (AIC, Akaike information), или байесовского информационного критерия (BIC, Bayesian information).
opt_gmm = Optimal_Clusters_GMM(dat, max_clusters = 10, criterion = "BIC", dist_mode = "maha_dist", seed_mode = "random_subset", km_iter = 10, em_iter = 10, var_floor = 1e-10, plot_data = T)При выборе модели из предопределенного множества предпочтительнее выбирать ту, у которой самый низкий BIC, здесь это справедливо для количества кластеров, равного 2.
Предполагая, что доступны метки истинности, для валидации выходных кластеров можно использовать методы external_validation (rand_index, adjusted_rand_index, jaccard_index, fowlkes_Mallows_index, mirkin_metric, purity, entropy, nmi (нормализованная взаимная информация) и var_info (вариация информации).
res = external_validation(dietary_survey_IBS$class, pr$cluster_labels, method = "adjusted_rand_index", summary_stats = T) res ## ## ---------------------------------------- ## purity : 1 ## entropy : 0 ## normalized mutual information : 1 ## variation of information : 0 ## ---------------------------------------- ## specificity : 1 ## sensitivity : 1 ## precision : 1 ## recall : 1 ## F-measure : 1 ## ---------------------------------------- ## accuracy OR rand-index : 1 ## adjusted-rand-index : 1 ## jaccard-index : 1 ## fowlkes-mallows-index : 1 ## mirkin-metric : 0 ## ---------------------------------------- И если параметр summary_stats установлен в TRUE, то возвращаются также метрики специфичности, чувствительности, точности, полноты, F-меры (specificity, sensitivity, precision, recall, F-measure соответственно).
Метод k-средних
Кластеризация методом k-средних - метод векторного квантования, исходно применяемый в обработке сигналов, часто используется для кластерного анализа данных. Цель кластеризации методом k-средних - разделить n значений на k кластеров, в которых каждое значение принадлежит кластеру с ближайшим средним, выступающим прототипом кластера. Это приводит к разделению области данных на ячейки Вороного. Наиболее часто применяемый алгоритм использует итеративную уточняющую технику. Из-за повсеместного употребления, его называют алгоритмом k-средних; в частности, среди специалистов в сфере компьютерных наук он также известен как алгоритм Ллойда.
Пакет ClusterR предоставляет две разных функции k-средних, KMeans_arma, реализацию на R метода k-средних из библиотеки armadillo, и KMeans_rcpp, которая использует пакет RcppArmadillo. Обе функции приводят к одним и тем же результатам, однако, возвращают разные признаки (код ниже иллюстрирует это).
KMeans_arma
KMeans_arma быстрее, чем функция KMeans_rcpp, однако, исходно она выводит центроиды только некоторых кластеров. Более того, количество колонок в данных должно превышать количество кластеров, иначе функция вернет ошибку. Кластеризация будет работать быстрее на многоядерных машинах с включенным OpenMP (например, -fopenmp в GCC). Алгоритм инициализируется один раз, и обычно 10 итераций достаточно для сходимости. Исходные центроиды распределяются с помощью одного из алгоритмов - keep_existing, static_subset, random_subset, static_spread или random_spread. Если seed_mode равно keep_existing, пользователь должен передать на вход матрицу центроидов.
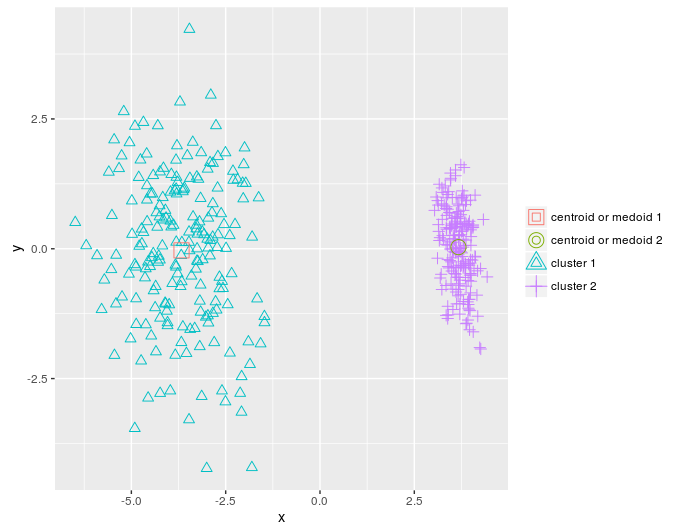
Я уменьшу количество измерений в данных dietary_survey_IBS с помощью анализа главных компонент (PCA - principal component analysis), а именно - функции princomp из пакета stats, чтобы можно было вывести двумерный график кластеров, построенных в результате.
pca_dat = stats::princomp(dat)$scores[, 1:2] km = KMeans_arma(pca_dat, clusters = 2, n_iter = 10, seed_mode = "random_subset", verbose = T, CENTROIDS = NULL) pr = predict_KMeans(pca_dat, km) table(dietary_survey_IBS$class, pr) class(km) = 'matrix' plot_2d(data = pca_dat, clusters = as.vector(pr), centroids_medoids = as.matrix(km)) 
KMeans_rcpp
Как утверждалось выше, функция KMeans_rcpp предлагает некоторые дополнительные возможности по сравнению с функцией KMeans_arma:
- она позволяет более одной инициализации (можно параллелизировать с OpenMP)
- помимо инициализаций с optimal_init, quantile_init, random или kmeans++, можно задать центроиды в параметре CENTROIDS
- время работы алгоритма и его сходимость можно настраивать параметрами num_init, max_iters и tol
- если num_init > 1, KMeans_rcpp возвращает атрибуты лучшей инициализации, используя критерий within-cluster-sum-of-squared-error (сумма-квадратов-ошибок-внутри-кластера)
- алгоритм возвращает следующие атрибуты: clusters, fuzzy_clusters (если fuzzy = TRUE), centroids, total_SSE, best_initialization, WCSS_per_cluster, obs_per_cluster, between.SS_DIV_total.SS
Больше подробностей о KMeans_rcpp есть в документации пакета. Проиллюстрирую разные параметры KMeans_rcpp на примере векторного квантования и пакета OpenImageR.
library(OpenImageR) path = 'elephant.jpg' im = readImage(path) # сначала изменим размер картинки, чтобы уменьшить количество измерений im = resizeImage(im, 75, 75, method = 'bilinear') imageShow(im) # вывод исходного изображения im2 = apply(im, 3, as.vector) # векторизированный RGB 
# кластеризация с KMeans_rcpp km_rc = KMeans_rcpp(im2, clusters = 5, num_init = 5, max_iters = 100, initializer = 'optimal_init', threads = 1, verbose = F) km_rc$between.SS_DIV_total.SS ## [1] 0.9873009 Атрибут between.SS_DIV_total.SS равен (total_SSE - sum(WCSS_per_cluster)) / total_SSE. Если в кластеризации нет закономерности, промежуточная сумма квадратов будет очень небольшой частью общей суммы квадратов, а если атрибут between.SS_DIV_total.SS близок к 1.0, значения кластеризуются достаточно хорошо.
getcent = km_rc$centroids getclust = km_rc$clusters new_im = getcent[getclust, ] # каждое значение ассоциируется с ближайшим центроидом dim(new_im) = c(nrow(im), ncol(im), 3) # обратное преобразование к трехмерной картинке imageShow(new_im) 
Кроме того, можно воспользоваться функцией Optimal_Clusters_KMeans (которая неявно использует KMeans_rcpp), чтобы определить оптимальное количество кластеров. Доступны такие критерии: variance_explained, WCSSE (within-cluster-sum-of-squared-error - сумма-квадратов-ошибок-внутри-кластера), dissimilarity, silhouette, distortion_fK, AIC, BIC и Adjusted_Rsquared. В документации по пакету есть больше информации по каждому критерию.
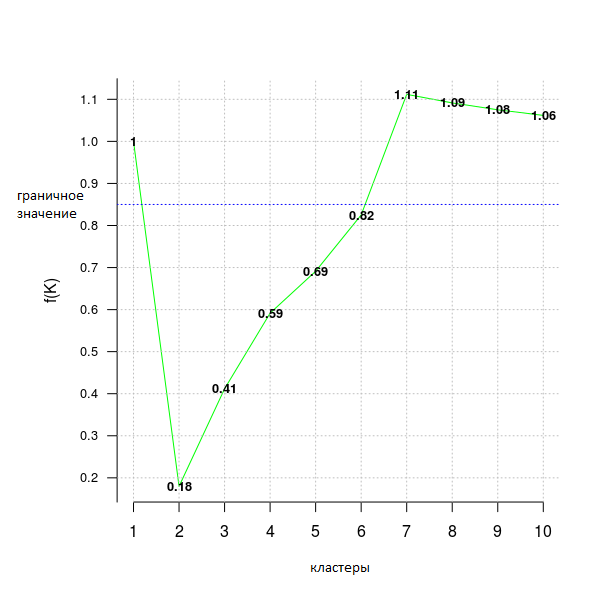
В следующем примере кода используется критерий distortion_fK, который полностью описан в статье -Selection of K in K-means clustering, Pham., Dimov., Nguyen., (2004)- («Выбор К в кластеризации методом К-средних»).
opt = Optimal_Clusters_KMeans(im2, max_clusters = 10, plot_clusters = T, verbose = F, criterion = 'distortion_fK', fK_threshold = 0.85)
Значения меньше фиксированной границы (здесь fK_threshold = 0.85) можно рекомендовать для кластеризации. Однако, существует более одного оптимального разбиения на кластеры, поэтому f(K) следует использовать только для предположения об их количестве, но окончательное решение, принимать это значение или нет - за пользователем.
Метод k-средних в мини-группах
Метод k-средних в мини-группах - вариация классического алгоритма k-средних. Он особенно полезен для больших наборов данных, поскольку вместо использования всего набора (как в k-средних) берутся мини-группы из случайных значений данных, чтобы оптимизировать целевую функцию.
Параметры алгоритма MiniBatchKmeans почти такие же, как и функции KMeans_rcpp из пакета ClusterR. Наиболее важная разница - параметр batch_size (размер мини-групп) и init_fraction (процент данных для определения исходных центроидов, который применяется, если initializer равен -kmeans++- или -quantile_init-).
Воспользуюсь примером векторного квантования, чтобы показать разницу во времени вычисления и качестве вывода функций KMeans_rcpp и MiniBatchKmeans.
path_d = 'dog.jpg' im_d = readImage(path_d) # сначала изменим размер картинки, чтобы уменьшить количество измерений im_d = resizeImage(im_d, 350, 350, method = 'bilinear') imageShow(im_d) # вывод исходного изображения 
im3 = apply(im_d, 3, as.vector) # векторизированный RGB dim(im3) # исходные измерения данных # 122500 3 Сначала выполним кластеризацию k-средних.
start = Sys.time() km_init = KMeans_rcpp(im3, clusters = 5, num_init = 5, max_iters = 100, initializer = 'kmeans++', threads = 1, verbose = F) end = Sys.time() t = end - start cat('time to complete :', t, attributes(t)$units, '
') # время выполнения : 2.44029 secs getcent_init = km_init$centroids getclust_init = km_init$clusters new_im_init = getcent_init[getclust_init, ] # каждое значение ассоциируется с ближайшим центроидом dim(new_im_init) = c(nrow(im_d), ncol(im_d), 3) # обратное преобразование к трехмерной картинке imageShow(new_im_init) 
Теперь кластеризацию k-средних в мини-группах.
start = Sys.time() km_mb = MiniBatchKmeans(im3, clusters = 5, batch_size = 20, num_init = 5, max_iters = 100, init_fraction = 0.2, initializer = 'kmeans++', early_stop_iter = 10, verbose = F) pr_mb = predict_MBatchKMeans(im3, km_mb$centroids) end = Sys.time() t = end - start cat('time to complete :', t, attributes(t)$units, '
') # время выполнения : 0.8346727 secs getcent_mb = km_mb$centroids new_im_mb = getcent_mb[pr_mb, ] # каждое значение ассоциируется с ближайшим центроидом dim(new_im_mb) = c(nrow(im_d), ncol(im_d), 3) # обратное преобразование к трехмерной картинке imageShow(new_im_mb) 
Несмотря на небольшую разницу в качестве вывода, k-средних в мини-группах возвращает результат в среднем в два раза быстрее, чем классический метод k-средних для этого набора данных.
Чтобы реализовать метод k-средних в мини-группах, я использовал следующие ресурсы:
- www.eecs.tufts.edu/~dsculley/papers/fastkmeans.pdf
- github.com/siddharth-agrawal/Mini-Batch-K-Means
- github.com/scikit-learn/scikit-learn/blob/51a765a/sklearn/cluster/k_means_.py#L1113
Телеграм: t.me/ainewsline
Источник: habrahabr.ru